Datenwissenschaft und maschinelles Lernen (Teil 18): Der Kampf um die Beherrschung der Marktkomplexität, verkürzte SVD versus NMF
-- Je mehr man hat, desto weniger sieht man!
Inhalt:
- Was ist Dimensionsreduktion?
- Hochdimensionale Daten
- Fluch der Dimensionalität
- Was bedeutet verkürzte SVD?
- Berechnung der Funktion der erklärten Varianz
- Dimensionsreduktion mit verkürzter SVD
- Vorteile der verkürzten SVD
- Vorteile des NMF
- Nachteile der verkürzten SVD
- Nachteile des NMF
- Kompromisse bei der Dimensionsreduktion
- FAQs zur Dimensionsreduktion
Dimensionsreduktion
Laut Wikipedia ist die Dimensionsreduktion die Umwandlung von Daten aus einem hochdimensionalen Raum in einen niedrigdimensionalen Raum, sodass die niedrigdimensionale Darstellung einige sinnvolle Eigenschaften der ursprünglichen Daten beibehält, idealerweise nahe an ihrer intrinsischen Dimension.
Die Arbeit in hochdimensionalen Räumen kann aus vielen Gründen unerwünscht sein; die Rohdaten sind oft dünnbesetzt als Folge des Fluchs der Dimensionalität, und die Analyse der Daten ist in der Regel rechnerisch schwer zu bewältigen (schwer zu kontrollieren oder zu verarbeiten). Dimensionsreduktion ist in Bereichen üblich, die sich mit einer großen Anzahl von Beobachtungen und/oder einer großen Anzahl von Variablen befassen, wie z. B. Signalverarbeitung, Spracherkennung, Neuroinformatik und Bioinformatik, mehr dazu hier.
Nachfolgend sind einige wichtige Punkte der Dimensionsreduktion aufgeführt.
Hochdimensionale Daten
In den meisten realen Anwendungen haben viele Datensätze, die zur Erstellung von Machine-Learning-Modellen verwendet werden, eine sehr große Anzahl von Merkmalen oder Variablen (Dimensionen). Hochdimensionale Daten können zu allen möglichen Herausforderungen führen, z. B. zu einer erhöhten Berechnungskomplexität, dem Risiko einer Überanpassung und Schwierigkeiten bei der Visualisierung. Der Datensatz, den Sie normalerweise mit 5 unabhängigen Variablen verwenden, ist nicht das, was die großen Jungs im algorithmischen KI-Handel tun.
Sagen wir, wir sammeln alle MT5(38) eingebauten Indikatorpuffer, am Ende haben wir 56 Puffer mit Daten. Dieser Datensatz ist jetzt riesig.
Fluch der Dimensionalität
Dieser Fluch ist real, und wer das nicht glaubt, kann versuchen, ein lineares Regressionsmodell mit vielen korrelierten unabhängigen Variablen zu implementieren.Das Vorhandensein von stark korrelierten Merkmalen kann dazu führen, dass die Modelle für maschinelles Lernen das Rauschen und die spezifischen Muster in den Trainingsdaten erfassen, die sich möglicherweise nicht gut auf neue, ungesehene Daten übertragen lassen.
Der Fluch der Dimensionalität bezieht sich auf die Probleme, die beim Umgang mit hochdimensionalen Daten auftreten, wie z. B. dünnbesetzte Datenverteilung, erhöhter Rechenaufwand und das Risiko einer Überanpassung des Modells, mehr dazu hier.
Lassen Sie mich dies anhand eines linearen Regressionsmodells näher erläutern:
Da es sich bei den ersten 13 Indikatoren in der CSV-Datei um trendfolgende Indikatoren handelt, ist es sehr wahrscheinlich, dass sie mit sich selbst und mit dem Markt korrelieren, obwohl sie unterschiedliche Dimensionen haben.
Wenn nur 10 Trendfolge-Indikatoren verwendet wurden, um die Schlusskurse für 100 Balken mit unserem linearen Regressionsmodell vorherzusagen:
matrix_utils.TrainTestSplitMatrices(data, train_x, train_y, test_x, test_y); lr.fit(train_x, train_y, NORM_MIN_MAX_SCALER); vector preds = lr.predict(train_x); Print("Train acc = ",metrics.r_squared(train_y, preds));
Das Ergebnis war ein Modell mit einer Genauigkeit von 92,2 % in der Trainingsphase.
IH 0 16:02:57.760 dimension reduction test (EURUSD,H1) Train acc = 0.9222314640780123
Sogar die Vorhersagen waren so genau.
KE 0 07:10:55.652 GetAllIndicators Data (EURUSD,H1) Actuals GS 0 07:10:55.652 GetAllIndicators Data (EURUSD,H1) [1.100686090182938,1.092937381937508,1.092258894809645,1.092946246629209,1.092958015748051,1.093392517797872,1.091850551839335,1.093040013995282,1.10067748979471,1.09836069904319,1.100275794247118,1.09882067865937,1.098572498565924,1.100543446136921,1.093174625248424,1.092435707204331,1.094128601953777,1.094192935809526,1.100305866167228,1.098452358470866,1.093010702771546,1.098612431849777,1.100827466038129,1.092880150279397,1.092600810699407,1.098722104612313,1.100707460497776,1.09582736814953,1.093765475161778,1.098767398966827,1.099091982657956,1.1006214183736,1.100698195592653,1.092047903797313,1.098661598784805,1.098489471676998,1.0997812203466,1.091954251247136,1.095870956581002,1.09306319770129,1.092915244023817,1.09488564050598,1.094171202526975,1.092523345374652,1.100564904733422,1.094200831112628,1.094001716368673,1.098530017588284,1.094081896433971,1.099230887219729,1.092892028948739,1.093709694144579,1.092862170694582,1.09148709705318,1.098520929394599,1.095105152264984,1.094272325978734,1.098468177450342,1.095849714911251,1.097952718476183,1.100746388049607,1.100114369109941,1.10052138086191,1.096938196194811,1.099992890418429,1.093106549957034,1.095523586088275,1.092801661288758,1.095956895328893,1.100419992807803] PO 0 07:10:55.652 GetAllIndicators Data (EURUSD,H1) Preds DH 0 07:10:55.652 GetAllIndicators Data (EURUSD,H1) [1.10068609018278,1.092937381937492,1.092258894809631,1.09294624662921,1.092958015748061,1.093392517797765,1.091850551839298,1.093040013995258,1.100677489794526,1.098360699043097,1.100275794246983,1.098820678659222,1.09857249856584,1.1005434461368,1.093174625248397,1.09243570720428,1.094128601953754,1.094192935809492,1.100305866167089,1.098452358470756,1.09301070277155,1.098612431849647,1.100827466038003,1.092880150279385,1.092600810699346,1.098722104612175,1.100707460497622,1.095827368149497,1.093765475161723,1.098767398966682,1.099091982657809,1.100621418373435,1.100698195592473,1.092047903797267,1.098661598784675,1.098489471676911,1.099781220346472,1.091954251247108,1.095870956580967,1.09306319770119,1.092915244023811,1.094885640505868,1.094171202526922,1.092523345374596,1.100564904733304,1.094200831112605,1.094001716368644,1.098530017588172,1.094081896433954,1.099230887219588,1.092892028948737,1.093709694144468,1.092862170694582,1.091487097053125,1.098520929394468,1.09510515226494,1.094272325978626,1.098468177450255,1.095849714911142,1.097952718476091,1.100746388049438,1.100114369109807,1.100521380861786,1.096938196194706,1.099992890418299,1.093106549956975,1.09552358608823,1.092801661288665,1.095956895328861,1.100419992807666]
Ich glaube, wir sind uns einig, dass dies zu schön ist, um wahr zu sein. Obwohl das Modell eine beeindruckende Genauigkeit von 87,5 % in der Teststichprobe aufweist, sinkt die Genauigkeit um etwa 5 %.
IJ 0 16:02:57.760 dimension reduction test (EURUSD,H1) Test acc = 0.8758590697252272
Wir können die gängigste Technik zur Dimensionsreduzierung, die Hauptkomponentenanalyse (PCA), verwenden, um die Dimensionen unseres Datensatzes zu reduzieren, der jetzt 10 Spalten hat.
//--- Reduce dimension pca = new CPCA(8); //Reduce the dimensions of the data to 8 columns data = pca.fit_transform(data); pca.extract_components(data, CRITERION_SCREE_PLOT);
Das Ergebnis war ein lineares Regressionsmodell mit einer Genauigkeit von 88,98 % beim Training und 89,991 % beim Testen, wobei die Genauigkeit gelinde gesagt nicht abnahm.
DJ 0 16:03:23.890 dimension reduction test (EURUSD,H1) Train acc = 0.8898608919375138 RH 0 16:03:23.890 dimension reduction test (EURUSD,H1) Test acc = 0.8991693574000851
Es ist immer noch ein überangepasstes Modell, aber viel besser als ein 92% genaues Modell, wenn es um die Fähigkeit zur Verallgemeinerung geht, die für ein ML-Modell von entscheidender Bedeutung ist. Sie können die Dimensionen weiter reduzieren, um zu sehen, welche Dimensionen der Daten die besten Ergebnisse bei Vorhersagen außerhalb der Stichprobe liefern.
Motivation für die Dimensionsreduktion
- Effiziente Berechnung: Die Verringerung der Anzahl der Dimensionen kann das Training und die Ausführung von Algorithmen für maschinelles Lernen beschleunigen.
- Verbesserte Verallgemeinerung: Die Dimensionsreduktion kann dazu beitragen, die Fähigkeit eines Modells zur Verallgemeinerung auf neue, ungesehene Daten zu verbessern, so wie wir es im Beispiel des linearen Regressionsmodells gesehen haben.
- Visualisierung: Das vereinfacht die Visualisierung und Interpretation von Daten im niedrigdimensionalen Raum und fördert das menschliche Verständnis.
Was bedeutet verkürzte SVD?
Verkürzte Singulärwertzerlegung (Truncated SVD) ist eine Technik zur Dimensionsreduzierung, die wie andere Techniken zur Dimensionalitätsreduzierung die Dimensionen hochdimensionaler Daten reduziert und dabei den Großteil der ursprünglichen Informationen beibehält. Diese Technik ist besonders nützlich in Szenarien, in denen die Daten eine große Anzahl von Merkmalen aufweisen, was die Durchführung effizienter Berechnungen oder die Visualisierung der Daten erschwert.
Es handelt sich um eine Variante der Singulärwertzerlegung (SVD), die die ursprüngliche Matrix annähert, indem sie nur die obersten k Singulärwerte und ihre entsprechenden Singulärvektoren beibehält.
Theorie:
Bildquelle: Wikipedia
Gegeben sei eine Matrix ![]() mit den Dimensionen
mit den Dimensionen ![]() ×
× ![]() ist die Singulärwertzerlegung von
ist die Singulärwertzerlegung von ![]() gegeben durch:
gegeben durch:
![]()
wobei:
![]() eine orthogonale Matrix
eine orthogonale Matrix ![]() ×
× ![]() (linke singuläre Vektoren) ist,
(linke singuläre Vektoren) ist,
![]() eine
eine ![]() ×
× ![]() Diagonalmatrix mit Singulärwerten auf der Diagonalen ist,
Diagonalmatrix mit Singulärwerten auf der Diagonalen ist,
![]() eine orthogonale Matrix
eine orthogonale Matrix ![]() ×
× ![]() (rechte singuläre Vektoren) ist.
(rechte singuläre Vektoren) ist.
Bei der verkürzten SVD werden nur die obersten k Singulärwerte und die entsprechenden Vektoren gespeichert:
wobei:
![]() ist eine
ist eine ![]() ×
× ![]() Matrix,
Matrix,
![]() eine
eine ![]() ×
× ![]() Diagonalmatrix ist,
Diagonalmatrix ist,
![]() eine
eine ![]() ×
× ![]() Matrix ist.
Matrix ist.
Umsetzung:
matrix CTruncatedSVD::fit_transform(matrix &X) { n_features = X.Cols(); if (m_components>n_features) { printf("%s Number of dimensions K[%d] is supposed to be <= number of features %d",__FUNCTION__,m_components,n_features); this.m_components = (uint)n_features; } // Center the data (subtract mean) matrix X_centered = CDimensionReductionHelpers::subtract(X, X.Mean(0)); // Compute the covariance matrix matrix cov_matrix = X_centered.Cov(false); // Perform SVD on the covariance matrix matrix U, Vt; vector Sigma; if (!X_centered.SVD(U,Vt,Sigma)) Print(__FUNCTION__," Line ",__LINE__," Failed to calculate SVD Err=",GetLastError()); this.components_ = CDimensionReductionHelpers::Slice(Vt, this.m_components).Transpose(); if (MQLInfoInteger(MQL_DEBUG)) Print("components\n",CDimensionReductionHelpers::Slice(Vt, this.m_components),"\ncomponents_T\n",this.components_); this.explained_variance_ = MathPow(CDimensionReductionHelpers::Slice(Sigma, this.m_components), 2) / (X.Rows() - 1); return X_centered.MatMul(components_); }
Es gibt eine eingebaute MQL5-Methode zur Berechnung der SVD einer Matrix.
// Singular Value Decomposition. bool matrix::SVD( matrix& U, // unitary matrix matrix& V, // unitary matrix vector& singular_values // singular values vector );
Die Funktion fit_transform bewirkt Folgendes:
- Sie zentriert die Daten durch Subtraktion des Mittelwerts.
- Sie berechnet die Kovarianzmatrix der zentrierten Daten (nicht wichtig).
- Sie führt SVD mit der Kovarianzmatrix durch.
- Sie behält die obersten k Singulärwerte und Vektoren.
- Sie konstruiert die reduzierte dimensionale Darstellung der ursprünglichen Matrix.
Berechnung der Funktion der erklärten Varianz
Die Funktion berechnet die Gesamtvarianz durch Summierung der Quadrate aller Einzelwerte.
ulong CTruncatedSVD::_select_n_components(vector &singular_values) { double total_variance = MathPow(singular_values.Sum(), 2); vector explained_variance_ratio = MathPow(singular_values, 2).CumSum() / total_variance; if (MQLInfoInteger(MQL_DEBUG)) Print(__FUNCTION__," Explained variance ratio ",explained_variance_ratio); vector k(explained_variance_ratio.Size()); for (uint i=0; i<k.Size(); i++) k[i] = i+1; plt.ScatterCurvePlots("Explained variance plot",k,explained_variance_ratio,"variance","components","Variance"); return explained_variance_ratio.ArgMax() + 1; //Choose k for maximum explained variance }Die Funktion nimmt ein Array von Singulärwerten (singular_values) als Eingabe. Diese Singulärwerte werden aus der Singulärwert-Zerlegung (Singular Value Decomposition, SVD) einer Matrix gewonnen.
Die Funktion wählt dann die Anzahl der Komponenten (k) aus, indem sie die Anzahl der Komponenten k mit der größten Varianz ermittelt. Dies wird mit dieser Codezeile erreicht:
explained_variance_ratio.ArgMax() + 1; Wir müssen unsere Funktion fit_transform so ändern, dass sie in der Lage ist, die beste Anzahl von Komponenten zu ermitteln (wenn keine Zahl angegeben ist), um die Dimensionen der Daten zu reduzieren und die Anzahl der Komponenten für die verkürzte SVD anzuwenden.
matrix CTruncatedSVD::fit_transform(matrix &X) { n_features = X.Cols(); if (m_components>n_features) { printf("%s Number of dimensions K[%d] is supposed to be <= number of features %d",__FUNCTION__,m_components,n_features); this.m_components = (uint)n_features; } // Center the data (subtract mean) matrix X_centered = CDimensionReductionHelpers::subtract(X, X.Mean(0)); // Compute the covariance matrix matrix cov_matrix = X_centered.Cov(false); // Perform SVD on the covariance matrix matrix U, Vt; vector Sigma; if (!cov_matrix.SVD(U,Vt,Sigma)) Print(__FUNCTION__," Line ",__LINE__," Failed to calculate SVD Err=",GetLastError()); if (m_components == 0) { m_components = (uint)this._select_n_components(Sigma); Print(__FUNCTION__," Best value of K = ",m_components); } this.components_ = CDimensionReductionHelpers::Slice(Vt, this.m_components).Transpose(); if (MQLInfoInteger(MQL_DEBUG)) Print("components\n",CDimensionReductionHelpers::Slice(Vt, this.m_components),"\ncomponents_T\n",this.components_); this.explained_variance_ = MathPow(CDimensionReductionHelpers::Slice(Sigma, this.m_components), 2) / (X.Rows() - 1); return X_centered.MatMul(components_); }
Der Standardwert k ist jetzt auf Null gesetzt, damit dies mühelos möglich ist.
CTruncatedSVD::CTruncatedSVD(uint k=0) :m_components(k) { }
Dimensionsreduktion mit verkürzter SVD
Schauen wir uns nun an, wie sich die durch die verkürzte SVD in der Dimension reduzierten Daten verhalten:
truncated_svd = new CTruncatedSVD(); data = truncated_svd.fit_transform(data); Print("Reduced matrix\n",data); //--- matrix train_x, test_x; vector train_y, test_y; data = matrix_utils.concatenate(data, target); //add the target variable to the dataset that is either normalized or not matrix_utils.TrainTestSplitMatrices(data, train_x, train_y, test_x, test_y, 0.7, 42); lr.fit(train_x, train_y, NORM_STANDARDIZATION); //training Linear regression model vector preds = lr.predict(train_x); //Predicting the training data Print("Train acc = ",metrics.r_squared(train_y, preds)); //Measuring the performance preds = lr.predict(test_x); //predicting the test data Print("Test acc = ",metrics.r_squared(test_y, preds)); //measuring the performance
Ausgaben:
LH 0 20:13:41.385 dimension reduction test (EURUSD,H1) CTruncatedSVD::_select_n_components Explained variance ratio [0.2399955100411572,0.3875113031818686,0.3903532427910986,0.3929609228375971,0.3932960517565894,0.3933072531960168,0.3933072531960282,0.3933072531960282,0.3933072531960282,0.3933072531960282] EH 0 20:13:41.406 dimension reduction test (EURUSD,H1) CTruncatedSVD::fit_transform Best value of K = 7 ... ... ... MR 0 20:13:41.407 dimension reduction test (EURUSD,H1) Train acc = 0.8934645199970468 HP 0 20:13:41.407 dimension reduction test (EURUSD,H1) Test acc = 0.8988671205298875
Eine erstaunliche und stabile Leistung: 89,3% Genauigkeit beim Training und 89,8% Genauigkeit beim Testen. Was ist mit dem NMF?
Was ist der NMF?
NMF steht für Non-Negative Matrix Factorization (nicht-negative Matrixzerlegung) und ist ein Verfahren zur Dimensionsreduktion, das eine Matrix in zwei nicht-negative Matrizen zerlegt. Ziel der NMF ist es, die ursprüngliche Matrix als Produkt zweier niedrigdimensionaler Matrizen darzustellen, wobei alle Elemente in den Matrizen nicht-negativ sind.
Bei einer Eingabematrix X der Dimensionen m×n zerlegt NMF diese in zwei Matrizen W und H, sodass:
![]()
Wobei:
![]() ist eine
ist eine ![]() ×
× ![]() Matrix, wobei k die Anzahl der Komponenten oder Merkmale ist.
Matrix, wobei k die Anzahl der Komponenten oder Merkmale ist.
![]() ist eine
ist eine ![]() ×
× ![]() Matrix.
Matrix.
Sowohl ![]() als auch
als auch ![]() haben nicht-negative Einträge, und diese Einschränkung der Nicht-Negativität macht die NMF besonders geeignet für Anwendungen, bei denen die Daten von Natur aus nicht-negativ sind, wie z. B. Bilddaten, Textdaten und Spektrogramme.
haben nicht-negative Einträge, und diese Einschränkung der Nicht-Negativität macht die NMF besonders geeignet für Anwendungen, bei denen die Daten von Natur aus nicht-negativ sind, wie z. B. Bilddaten, Textdaten und Spektrogramme.
Die Faktorisierung erfolgt durch Minimierung der Frobenius-Norm der Differenz zwischen der Originalmatrix ![]() und ihrer Approximation
und ihrer Approximation ![]() ×
× ![]() . Mathematisch kann dies wie folgt ausgedrückt werden:
. Mathematisch kann dies wie folgt ausgedrückt werden:
![]()
wobei ![]() die Frobenius-Norm bezeichnet.
die Frobenius-Norm bezeichnet.
Umsetzung:
Transformationsmethode
matrix CNMF::transform(matrix &X) { n_features = X.Cols(); if (m_components>n_features) { printf("%s Number of dimensions K[%d] is supposed to be <= number of features %d",__FUNCTION__,m_components,n_features); this.m_components = (uint)n_features; } if (this.W.Rows()==0 || this.H.Rows()==0) { Print(__FUNCTION__," Model not fitted. Call fit method first."); matrix mat={}; return mat; } return X.MatMul(this.H.Transpose()); }
Die Transformationsfunktion transformiert neue Daten X unter Verwendung der bereits angepassten NMF-Komponenten.
Die Methode fit_transform
matrix CNMF::fit_transform(matrix &X, uint k=2) { ulong m = X.Rows(), n = X.Cols(); double best_frobenius_norm = DBL_MIN; m_components = m_components == 0 ? (uint)n : k; //--- Initialize Random values this.W = CMatrixutils::Random(0,1, m, this.m_components, this.m_randseed); this.H = CMatrixutils::Random(0,1,this.m_components, n, this.m_randseed); //--- Update factors vector loss(this.m_max_iter); for (uint i=0; i<this.m_max_iter; i++) { // Update W this.W *= MathAbs((X.MatMul(this.H.Transpose())) / (this.W.MatMul(this.H.MatMul(this.H.Transpose()))+ 1e-10)); // Update H this.H *= MathAbs((this.W.Transpose().MatMul(X)) / (this.W.Transpose().MatMul(this.W.MatMul(this.H))+ 1e-10)); loss[i] = MathPow((X - W.MatMul(H)).Flat(1), 2); // Calculate Frobenius norm of the difference double frobenius_norm = (X - W.MatMul(H)).Norm(MATRIX_NORM_FROBENIUS); if (MQLInfoInteger(MQL_DEBUG)) printf("%s [%d/%d] Loss = %.5f frobenius norm %.5f",__FUNCTION__,i+1,m_max_iter,loss[i],frobenius_norm); // Check convergence if (frobenius_norm < this.m_tol) break; } return this.W.MatMul(this.H); }
Die Methode fit_transform führt eine NMF-Zerlegung der Eingabematrix X durch und gibt das Produkt der Matrizen W und H zurück.
Im Gegensatz zur verkürzten SVD, bei der wir in der Lage waren, einen Code zu schreiben, um die Anzahl der Komponenten zu bestimmen und ihn auf sich selbst anzuwenden, was die Verwendung der verkürzten Bibliothek vereinfacht, ist der NMF-Lernalgorithmus ganz anders, da er eine Anzahl von n Iterationen erfordert, um die besten Werte für den Algorithmus zu finden. Während der Schleife muss die Anzahl der k Komponenten gleich bleiben, weshalb die Funktion fit_transform den Wert der k Komponenten als eines ihrer Argumente annimmt.
Mit der Funktion select_best_components können wir die beste Anzahl von Komponenten für den Algorithmus zur Faktorisierung der nichtnegativen Matrix ermitteln:
uint CNMF::select_best_components(matrix &X) { uint best_components = 1; this.m_components = (uint)X.Cols(); vector explained_ratio(X.Cols()); for (uint k = 1; k <= X.Cols(); k++) { // Calculate explained variance or other criterion matrix X_reduced = fit_transform(X, k); // Calculate explained variance as the ratio of squared Frobenius norms double explained_variance = 1.0 - (X-X_reduced).Norm(MATRIX_NORM_FROBENIUS) / (X.Norm(MATRIX_NORM_FROBENIUS)); if (MQLInfoInteger(MQL_DEBUG)) printf("k %d Explained Var %.5f",k,explained_variance); explained_ratio[k-1] = explained_variance; } return uint(explained_ratio.ArgMax()+1); }
Da sowohl die Basis- als auch die Koeffizientenmatrix Zufallswerte sind, sind auch die Ergebnisse des iterativen multiplikativen Algorithmus Zufallswerte, sodass das Ergebnis nicht vorhersehbar ist, es sei denn, der Zufallsstatus wird auf einen Wert größer als Null gesetzt.
class CNMF { protected: uint m_components; uint m_max_iter; int m_randseed; ulong n_features; matrix W; //Basic matrix matrix H; //coefficient matrix double m_tol; //loss tolerance public: CNMF(uint max_iter=100, double tol=1e-4, int random_state=-1); ~CNMF(void); matrix fit_transform(matrix &X, uint k=2); matrix transform(matrix &X); uint select_best_components(matrix &X); };
Dimensionsreduktion mit NMF
Sehen wir uns nun an, wie sich die durch nicht-negative Matrixzerlegung in der Dimension reduzierten Daten verhalten:
nmf = new CNMF(30); data = nmf.fit_transform(data, 10); Print("Reduced matrix\n",data); //--- matrix train_x, test_x; vector train_y, test_y; data = matrix_utils.concatenate(data, target); //add the target variable to the dataset that is either normalized or not matrix_utils.TrainTestSplitMatrices(data, train_x, train_y, test_x, test_y, 0.7, 42); lr.fit(train_x, train_y, NORM_STANDARDIZATION); //training Linear regression model vector preds = lr.predict(train_x); //Predicting the training data Print("Train acc = ",metrics.r_squared(train_y, preds)); //Measuring the performance preds = lr.predict(test_x); //predicting the test data Print("Test acc = ",metrics.r_squared(test_y, preds)); //measuring the performance
Ergebnisse:
DG 0 11:51:07.197 dimension reduction test (EURUSD,H1) Best k components = 10 LG 0 11:51:07.197 dimension reduction test (EURUSD,H1) CNMF::fit_transform [1/30] Loss = 187.40949 frobenius norm 141.12462 EG 0 11:51:07.198 dimension reduction test (EURUSD,H1) CNMF::fit_transform [2/30] Loss = 106.49597 frobenius norm 130.94039 KS 0 11:51:07.198 dimension reduction test (EURUSD,H1) CNMF::fit_transform [3/30] Loss = 84.38553 frobenius norm 125.05413 OS 0 11:51:07.198 dimension reduction test (EURUSD,H1) CNMF::fit_transform [4/30] Loss = 67.07345 frobenius norm 118.96900 OR 0 11:51:07.198 dimension reduction test (EURUSD,H1) CNMF::fit_transform [5/30] Loss = 52.50290 frobenius norm 112.46587 LR 0 11:51:07.198 dimension reduction test (EURUSD,H1) CNMF::fit_transform [6/30] Loss = 40.14937 frobenius norm 105.48081 RR 0 11:51:07.198 dimension reduction test (EURUSD,H1) CNMF::fit_transform [7/30] Loss = 29.79307 frobenius norm 98.11626 IR 0 11:51:07.198 dimension reduction test (EURUSD,H1) CNMF::fit_transform [8/30] Loss = 21.32224 frobenius norm 90.63011 NS 0 11:51:07.198 dimension reduction test (EURUSD,H1) CNMF::fit_transform [9/30] Loss = 14.63453 frobenius norm 83.36462 HL 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [10/30] Loss = 9.58168 frobenius norm 76.62838 NL 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [11/30] Loss = 5.95040 frobenius norm 70.60136 DM 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [12/30] Loss = 3.47775 frobenius norm 65.31931 LM 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [13/30] Loss = 1.88772 frobenius norm 60.72185 EN 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [14/30] Loss = 0.92792 frobenius norm 56.71242 RO 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [15/30] Loss = 0.39182 frobenius norm 53.19791 NO 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [16/30] Loss = 0.12468 frobenius norm 50.10411 NH 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [17/30] Loss = 0.01834 frobenius norm 47.37568 KI 0 11:51:07.199 dimension reduction test (EURUSD,H1) CNMF::fit_transform [18/30] Loss = 0.00129 frobenius norm 44.96962 KI 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [19/30] Loss = 0.02849 frobenius norm 42.84850 MJ 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [20/30] Loss = 0.07289 frobenius norm 40.97668 RJ 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [21/30] Loss = 0.11920 frobenius norm 39.31975 QK 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [22/30] Loss = 0.15954 frobenius norm 37.84549 FD 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [23/30] Loss = 0.19054 frobenius norm 36.52515 RD 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [24/30] Loss = 0.21142 frobenius norm 35.33409 KE 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [25/30] Loss = 0.22283 frobenius norm 34.25183 PF 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [26/30] Loss = 0.22607 frobenius norm 33.26170 GF 0 11:51:07.200 dimension reduction test (EURUSD,H1) CNMF::fit_transform [27/30] Loss = 0.22268 frobenius norm 32.35028 NG 0 11:51:07.201 dimension reduction test (EURUSD,H1) CNMF::fit_transform [28/30] Loss = 0.21417 frobenius norm 31.50679 CG 0 11:51:07.201 dimension reduction test (EURUSD,H1) CNMF::fit_transform [29/30] Loss = 0.20196 frobenius norm 30.72260 CP 0 11:51:07.201 dimension reduction test (EURUSD,H1) CNMF::fit_transform [30/30] Loss = 0.18724 frobenius norm 29.99074 ... ... FS 0 11:51:07.201 dimension reduction test (EURUSD,H1) Train acc = 0.604329883526616 IR 0 11:51:07.202 dimension reduction test (EURUSD,H1) Test acc = 0.5115967009955317
Die Funktion select_best_components fand heraus, dass die beste Anzahl von Komponenten 10 war, was der Anzahl der Spalten im Datensatz entspricht, den wir ihr gegeben haben. Man kann mit Fug und Recht behaupten, dass die Genauigkeit der Daten, die aus der NMF resultiert, wenn sie auf das lineare Regressionsmodell angewandt wird, durchschnittliche Ergebnisse von 61 % während des Trainings und 51 % während des Tests erbrachte, bevor wir zu dem Schluss kommen, dass TruncatedSVD in dieser Situation ein klarer Gewinner ist. Wir müssen jedoch die Tatsache anerkennen, dass die nicht-negative Matrixzerlegung (NMF) viel Programmierarbeit erfordert, damit sie funktioniert. Wenn sie richtig implementiert wird und mit einem besseren Lernalgorithmus als dem stochastischen Gradientenabstieg (SGD) oder einem anderen intelligenten Lernalgorithmus versehen ist, kann sie einen besseren Datensatz erzeugen als die grundlegenden Implementierungen beider Algorithmen! Die Verkürzte SVD hat gewonnen (allerdings nur auf dem Papier)
Mal sehen, wie beide mit großen Datenmengen abschneiden:
Wenden wir die gesamten Daten auf unsere Algorithmen an und messen, wie sie im gesamten Datensatz abschneiden würden. Dies gibt uns einen Anhaltspunkt dafür, welche Methode angewendet werden sollte, um die am besten komprimierten Daten für unser lineares Regressionsmodell zu erhalten.
Verkürzte SVD gegen NMF, die Schlacht
Dieses Mal wurden keine Daten gefiltert, sondern alle Indikatoren für die verkürzte SVD verwendet.
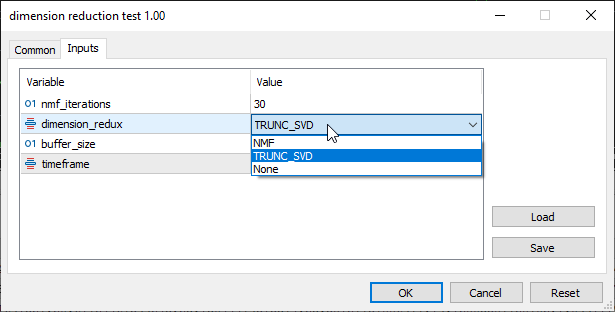
void TrainTestLR(int start_bar=1) { string names; matrix data = indicators.GetAllBuffers(names, start_bar, buffer_size); //--- Getting close values MqlRates rates[]; ArraySetAsSeries(rates, true); CopyRates(Symbol(), PERIOD_CURRENT, start_bar, buffer_size, rates); double targ_Arr[]; ArrayResize(targ_Arr, buffer_size); for (int i=0; i<buffer_size; i++) targ_Arr[i] = rates[i].close; vector target = matrix_utils.ArrayToVector(targ_Arr); //--- Dimension reduction process switch(dimension_redux) { case NMF: { nmf = new CNMF(nmf_iterations); uint k = nmf.select_best_components(data); //Print("Best k components = ",k); data = nmf.fit_transform(data, k); } break; case TRUNC_SVD: truncated_svd = new CTruncatedSVD(); data = truncated_svd.fit_transform(data); break; case None: break; } //--- Print(EnumToString(dimension_redux)," Reduced matrix[",data.Rows(),"x",data.Cols(),"]\n",data); //--- matrix train_x, test_x; vector train_y, test_y; data = matrix_utils.concatenate(data, target); //add the target variable to the dimension reduced data matrix_utils.TrainTestSplitMatrices(data, train_x, train_y, test_x, test_y, 0.7, 42); lr.fit(train_x, train_y, NORM_STANDARDIZATION); //training Linear regression model vector preds = lr.predict(train_x); //Predicting the training data Print("Train acc = ",metrics.r_squared(train_y, preds)); //Measuring the performance preds = lr.predict(test_x); //predicting the test data Print("Test acc = ",metrics.r_squared(test_y, preds)); //measuring the performance }
In der Eingabesektion wurde TRUNC_SVD ausgewählt, was für Truncated (verkürzte) SVD steht:
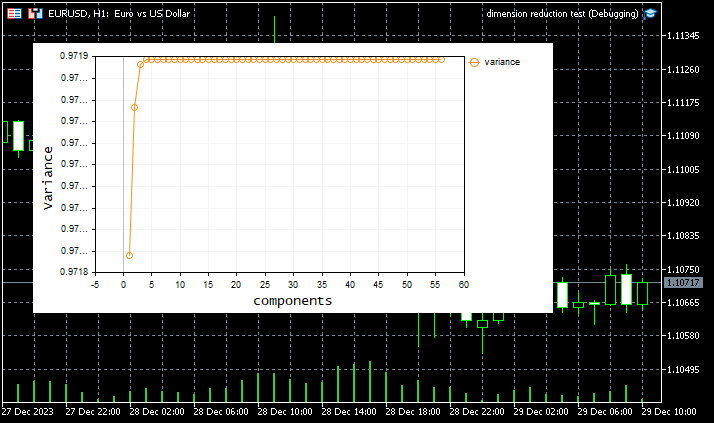
Die Ergebnisse waren erwartungsgemäß hervorragend für verkürzte SVD. Die Daten wurden in 11 nützliche Komponenten komprimiert, die sich am Drehpunkt der folgenden Grafik befinden
Ausgaben:
KI 0 13:35:07.262 dimension reduction test (EURUSD,H1) [56x56] Covariance HS 0 13:35:07.262 dimension reduction test (EURUSD,H1) [[1.659883222775595e-05,0.03248108864728622,0.002260592127494286,0.002331226815118805,0.0473802958063898,0.009411152185446843,-0.0007144995075063451,1.553267567351765e-05,1.94117385500497e-05,1.165361279698562e-05,1.596183979153003e-05,1.56892102141789e-05,1.565786314082391e-05,1.750827764889262e-05,1.568797564383075e-05,1.542116504856457e-05,1.305965012072059e-05,1.184306318548672e-05,0,1.578309112710041e-05,1.620880130984106e-05,3.200794587841053e-07,1.541769717649654e-05,1.582152318930163e-05,5.986572608120619e-07,-7.489818958341503e-07,-1.347949386573036e-07,1.358668593395908,-0.0551110816439555,7.279528408421348e-05,-0.0001838813666139953,5.310112938097826e-07,6.759105066381161e-07,1.755806692036581e-05,-1.448992128283333e-07,0.003656398187537544,-2.423948560741599e-05,1.65581437719033e-05,-0.01251289868226832,-0.007951606834421109,8.315844054428887e-08,-0.02211745766272421,58.3452835083685,-0.004138620879652527,115.0719348800515,0.7113815226449098,-3.467421230325816e-07,1.456828920113124e-05,1.536603660063518e-05,1.576222466715787e-05,6.85495465028602e-07,0,0,1.264184887739262e-06,-8.035590653384948e-05,-6.948836688267333e-07] DG 0 13:35:07.262 dimension reduction test (EURUSD,H1) [0.03248108864728622,197.2946284096305,47.5593359902222,-70.84984591299812,113.00968468357,80.50832448214619,-85.73100643892406,0.01887146397983594,0.03089371802428824,0.006849209935383654,0.03467670330041064,0.02416916876582018,0.02412087871833598,0.0345064443900023,0.03070601018237932,0.02036445858890056,0.009641324468627534,0.006973716378187099,0,0.02839705603036633,0.02546230398502955,0.000344615196142723,0.04030780408653764,0.02543558488321825,0.0003508232190957864,0.00918131954773614,0.009950700238139187,18501.50888551419,578.0227911644578,1.963532857377992,7.661630153435527,0.006966837168084083,0.004556433245004339,2.562261625497797,0.002410403923079745,118.382177007498,1.555763207775421,1.620640369180333,97.88352837129584,116.7606184094667,0.0006817870698682788,163.5401896749969,108055.4673427991,140.7005993870342,173684.2642498043,3567.96895955429,0.0026091195479834,0.01088219157686945,0.01632411390047346,0.02372834986595739,0.02071124643451263,0,0,0.003953688163493562,-1.360529605248643,-0.04542261766857811] IL 0 13:35:07.262 dimension reduction test (EURUSD,H1) [0.002260592127494286,47.5593359902222,39.19958980374253,-35.49971367926001,7.967839162735706,33.38887983973432,-33.90876164339727,-0.001453063639065681,-0.000297822858867019,-0.002608304419264346,0.002816269112655834,-0.0006711791217058063,-0.0006698381044796457,0.002120545460717355,0.002300146098203005,0.0001826452994732207,-0.0003768483866125172,-0.002445364564315893,0,0.0003665645439668078,-0.003400376924338417,-1.141907378821958e-06,0.006568498854351883,0.0006581929826678372,-0.0005502523415197902,0.00579179204268979,0.006348707171855972,7967.929705662135,452.5996105540225,0.7520153701277594,4.211592829265125,0.001461149548206051,0.0001367863805269901,0.8802824558924612,0.001324363167679062,50.70542641656378,0.6826775813408293,0.5131585731076505,116.3828090044126,97.64469627257866,5.244397974811099e-05,113.6246589165999,13312.60086575102,66.02007474397942,15745.06353439358,3879.735235353455,0.002648988695504766,-0.00244724050922883,-0.00263645588222185,-0.001438073133818628,0.005654239425742305,0,0,-0.000119694862927093,-0.3588916052856576,-0.1059287487094797] EM 0 13:35:07.262 dimension reduction test (EURUSD,H1) [0.002331226815118805,-70.84984591299812,-35.49971367926001,60.69058251292376,1.049456584665883,-42.35184208285295,60.90812761343581,0.008675881760275542,0.008620685402656748,0.008731078117894331,-0.000667294720674837,0.005845080481159768,0.005833401998679988,0.002539790385479495,0.001675796458760079,0.00792229604709134,0.01072137357191657,0.01189054942647922,0,0.003518070782066417,0.00809138574827074,0.0002045106345618818,-0.005848319055742076,0.005549764528898804,0.00103946798619902,-0.008604821519805591,-0.007960056731330659,-10509.62154107038,-607.7276555152829,-1.225906326607001,-5.179537786920108,-0.003656220590983723,-0.001714862736227047,-1.657652278786164,-0.001941357854756676,-80.61630801951124,-1.158614351229071,-1.010395372975761,-137.5151461158883,-129.0146405010356,…] DK 0 13:35:07.264 dimension reduction test (EURUSD,H1) CTruncatedSVD::_select_n_components Explained variance ratio [0.9718079496976207,0.971876424055512,0.9718966593387935,0.971898669685807,0.9718986697080317,0.9718986697081728,0.9718986697082533,0.9718986697082695,0.9718986697082731,0.9718986697082754,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757,0.9718986697082757] JJ 0 13:35:07.282 dimension reduction test (EURUSD,H1) CTruncatedSVD::fit_transform Best value of K = 11 FE 0 13:35:07.282 dimension reduction test (EURUSD,H1) components GP 0 13:35:07.282 dimension reduction test (EURUSD,H1) [[1.187125882554785e-07,1.707109381366902e-07,-2.162493440707256e-08,-3.212808990986057e-07,1.871672229653978e-07,-1.333159242305641e-05,-1.709658791626167e-05,5.106786021196193e-05,2.160157948893384e-05,-1.302989528292599e-06,4.973487699412528e-06,2.354866764130305e-06,0.0001127065022780296,-0.0001141032171988836,-7.674973628685988e-05,4.318893830956814e-06,-8.017085790662858e-05,1.258581118770149e-05,0.001793756756130711,0.0002550931459979332,0.0005154637372606566,0.001801147973070216,0.0001081777898713252,0.1803191282351903,-0.0971245889819613,0.1677985300894154,0.1116153850447159,0.6136670152098842,0.022810600805461,-0.4096528016535661,-0.04163009420605639,-6.077467743293966e-06,-0.01526638316446551,-0.5288520838909793,-0.03965140358106178,-0.1758179670991415,-0.003645717072725773,-0.0587633049540756,0.004124498383003558,-0.1172419838852104,0.06762215235985558,-0.04328191674666172,0.002573659612267772,0.003811049362514162,-0.0659455961610354,-0.02792883463906511,0.008647163802477509,-0.05514899696636823,0.008017364204121686,2.516946811168054e-06,-0.1623798112317545,6.339565837779877e-07,-9.103773865679859e-08,0,0,0] CH 0 13:35:07.282 dimension reduction test (EURUSD,H1) [0.000187434605818864,0.002812180913638008,0.000925532096115269,0.003073325320378009,0.009404433538995808,-0.1105512584754667,-0.2590049789665196,0.4726584971639716,0.1447383637844528,-0.05374370025421956,-0.752572111353205,0.04852191253671465,-0.1154729372340165,-0.2700032006603445,0.1267147455792905,-0.04806661586591762,-0.0004106947202907203,-0.001517506503982104,-0.003502569576390078,-0.002616630851275089,-0.0003258690084512006,-1.313122566421376e-05,-0.0009386837340425192,7.909925585103072e-05,-7.798476572374581e-05,-8.126463184191059e-05,5.556082790448295e-05,-2.687039190421141e-05,-6.540787996573879e-06,1.330764390715927e-05,-4.491635420079414e-05,-8.144156726118825e-06,-8.508538790002811e-07,5.307068574641107e-05,8.482440778162809e-06,-2.9724306932086e-05,2.843845070244019e-05,1.220433778827776e-05,4.206331251218703e-06,1.256512854012554e-05,7.365925693883173e-06,-1.116338606511276e-05,-2.071419560390051e-06,-3.218285979262829e-06,-1.138651025910271e-05,-7.728111919788928e-06,-4.653652137908648e-06,-9.580813709785919e-06,-1.028740118967147e-05,-6.979591632948435e-06,8.116615752437345e-06,1.763108270729631e-06,-4.348070304093866e-07,0,0,0] JR 0 13:35:07.282 dimension reduction test (EURUSD,H1) [1.848792316776081e-05,0.0008588118715707877,0.001008311173244842,0.002376194713912998,0.03118554398340165,0.07889519945845663,-0.07568381470451135,0.0286506682781276,-0.09873220604411656,-0.09161678196011247,-0.06574722506621368,-0.8477734032486133,-0.2533539865405071,0.01738574140899809,-0.2520128661222155,0.338533576002899,0.03018091859501061,0.03802772499047165,-0.001646103636389454,-0.00230341248842314,0.007310099460075021,-0.006012419384786831,-0.001413152018214914,2.142238614111051e-05,2.944210407515316e-05,-6.521097350129076e-05,4.95794487446122e-05,-8.706533732190571e-06,3.322659358695792e-05,-8.146689287415223e-07,7.338661273889888e-06,6.605547217087068e-06,9.447199984574336e-06,-5.17902002055696e-05,2.513872334761899e-06,-2.256988836110105e-05,-1.911456753589991e-05,-3.264899090321399e-05,-5.800966034108816e-06,1.84157480007614e-05,5.356185659483905e-06,-1.722849771456492e-05,1.407694486288703e-05,-7.853816348797691e-06,-1.555432680785718e-05,1.323568644672602e-05,-6.760913172750632e-06,-1.302135272406512e-05,-3.211793238456227e-06,5.802687671843603e-07,-4.280158053673846e-06,1.549960937140237e-06,-4.919157307518426e-07,0,0,0] ND 0 13:35:07.282 dimension reduction test (EURUSD,H1) [4.113935038265459e-05,-0.00163116425762962,-0.0006793200544509552,-0.002550542034446345,-0.0360619764220519,-0.05083503039040507,0.1457232134777539,-0.1319534223026893,-0.1000465688426969,0.03066773678926198,0.211126338548004,0.02610057183969087,-0.4621259104920466,-0.5881871797892803,0.5329599008633419,0.2326293789423069,-0.004192622153062945,-0.05839467173045784,0.002320319216461524,0.007699098543144081,-0.007658991162669676,-0.003166005488782055,-0.002283364895801648,0.0001978857108759482,9.652410400630472e-05,5.391765247424044e-05,-2.114027852314159e-05,-3.571496353187668e-06,6.919610375993553e-06,-2.388732546126286e-05,-1.795211964869842e-05,-4.375012411627235e-05,-6.279526099805299e-05,2.71361750709131e-06,-2.519904126359203e-05,-3.154274545518064e-05,-4.95034356619025e-05,4.982607182957078e-05,2.91223664932767e-05,7.266298957499022e-06,-5.27732883601878e-0…] QD 0 13:35:07.283 dimension reduction test (EURUSD,H1) TRUNC_SVD Reduced matrix[100x11] FJ 0 13:35:07.283 dimension reduction test (EURUSD,H1) [[3032.510155721446,0.6797958296629614,0.3147476036369294,-1.879105115460979,2.342311343896795,-1.444862488231156,1.72748820545895,9003.45453268309,6583.0037062413,11248.15180107277,7664.89601210886] QF 0 13:35:07.283 dimension reduction test (EURUSD,H1) [2613.746957390415,0.8994353272147151,0.2278876639409569,-1.833173521667439,2.422820504229084,-1.194855144516288,1.619766862896731,8730.428168136412,6321.389560496657,10843.26327739175,7319.502533761807] PE 0 13:35:07.283 dimension reduction test (EURUSD,H1) [2290.391536977857,0.8379176898463352,0.123448650655239,-1.79572777997295,2.553555290053082,-1.261720012039457,1.872612496522998,9359.431555011421,6628.023623123124,11573.90347441899,7725.564567458286] MG 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1793.638587775052,0.8840827856664026,-0.009259140368535656,-1.812929578463889,2.752934946133839,-1.194132624145421,2.137669035967074,10045.24774931484,6958.660329797975,12319.85906895874,8090.242616080116] IG 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1067.248927502046,0.9361386848947133,0.2824462001532311,-2.094258230827017,2.302295904768048,-0.9859566963069195,1.849760818059724,8852.426567434784,5936.081092995532,10850.91447636461,7048.244994007338] NK 0 13:35:07.283 dimension reduction test (EURUSD,H1) [875.831228770905,1.10630868463423,0.3875078994082357,-2.07189694520072,2.003365098290179,-0.8110375102176066,1.363090061871958,7086.981018896034,4689.12320342304,8755.082428498208,5718.774787652458] GK 0 13:35:07.283 dimension reduction test (EURUSD,H1) [750.5105412678478,1.58876151742295,0.4277968820488219,-2.495434492237099,2.546292376170158,-0.5828893757361142,1.468026541982692,8457.543559890122,5579.75159746014,10352.91442474459,6691.476688344664] EK 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1028.864261893481,1.737564309663063,0.6859148896559381,-2.576387294650619,2.22158096752311,-0.3483142589026745,0.9424367352835165,7447.770506698205,5028.271311988544,9145.898159310427,5970.749558054185] MJ 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1315.206321750198,1.599230058650526,1.006274380327883,-2.7208483981554,1.702262719567507,-0.3336344655640055,0.5851633683692923,6123.681144041253,4208.879528858515,7625.280231352584,5091.190116446857] PI 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1040.359603039049,2.015870643904685,1.297584348509677,-3.422661750068991,2.051984203691556,-0.1752179554187868,0.625382499042994,7446.846626605789,4973.286352001192,9200.911151239434,6040.469516939555] MJ 0 13:35:07.283 dimension reduction test (EURUSD,H1) [2056.827104147074,0.6969653180001977,0.5026500071613408,-1.539526411095017,1.333168361525386,-1.205142789226661,0.6457357287148752,4362.936467349854,3118.514061447938,5739.541487386377,4094.4444510553] KI 0 13:35:07.283 dimension reduction test (EURUSD,H1) [2595.720157415741,0.5163475309230526,0.7707831677360033,-1.609464385287863,0.6391376890497206,-1.091660522613616,0.2434028653397404,2245.471581325966,1932.755290423922,3219.551710692477,2600.234934440349] FJ 0 13:35:07.283 dimension reduction test (EURUSD,H1) [2000.813854424802,-0.1645196557230545,0.0271698872028618,-1.136148599089293,1.199419424319289,-1.596267278271581,1.616290624329739,4340.908808342276,3155.426978423527,5643.263654816839,4006.305187235153] GN 0 13:35:07.283 dimension reduction test (EURUSD,H1) [714.201770611258,0.3322650152566928,-0.128924730742915,-1.497052055771412,1.889908667964611,-1.18328154703613,2.040965402442796,6411.664479403819,4214.549479233159,7917.864243044486,5153.2871400763] PN 0 13:35:07.283 dimension reduction test (EURUSD,H1) [676.7845833423586,0.1119963611895549,-0.4614956061196153,-0.7783442013329294,1.680735950870798,-1.110059082233565,1.926793017792492,5379.745050208609,3591.380424598063,6620.153862582291,4307.434978894435] GL 0 13:35:07.283 dimension reduction test (EURUSD,H1) [766.9657214036708,0.3283061830008722,-0.3885600107901345,-1.031650548898253,1.912288786544761,-1.036499883901753,2.01321049032323,6312.725946828255,4249.957068368147,7723.98867795246,5012.0279192467] LN 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1272.697206108888,-0.3546159778199272,-0.7521309963906442,-0.1806331494361637,1.527697751794935,-1.486437217294949,2.136800392269752,5073.89079322631,3559.651506707118,6317.965379534476,4229.397904810504] RM 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1869.479624807111,-0.0175694426730242,-0.7678796689175619,-0.2643173159395689,1.862033543014759,-1.44967470564508,2.028361828380722,5639.625182760593,4124.447639836587,7033.466549718048,4777.911629224665] GN 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1936.02506453734,0.0845940044872068,-0.8282752540396139,-0.2824304083282199,1.982789807497455,-1.350085518779075,2.085883725566998,5911.195073473721,4372.189044548059,7316.534104301676,4945.624347822407] CR 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1844.238763352675,-0.4606751585910102,-1.187448989349241,0.2320045292554417,1.900279565663612,-1.62110507361112,2.534343850099422,5907.730651516376,4364.59879103891,7282.962351393813,4893.24121551531] ER 0 13:35:07.283 dimension reduction test (EURUSD,H1) [1716.303347926322,-0.2450617860724134,-0.9482067759826802,-0.03979477150523128,1.79416546386642,-1.453641927846228,2.284520496569503,5710.722665215339,4183.828568899002,7048.670774203967,4734.907606214866…] GP 0 13:35:07.283 dimension reduction test (EURUSD,H1) Train acc = 0.8087284075835584 ER 0 13:35:07.283 dimension reduction test (EURUSD,H1) Test acc = 0.7286157353628964
80 % Genauigkeit bei der Trainingsstichprobe und 72 % Genauigkeit bei der Teststichprobe.
Nicht-negative Matrix-Faktorisierung (NMF)
Andererseits war der NMF nicht in der Lage, irgendetwas von Wert zu produzieren, da alles, was aus ihm hervorging, ein nan-Wert (not a number) war. An diesem Punkt scheidet er aus dem Wettbewerb aus.
LK 0 13:43:09.997 dimension reduction test (EURUSD,H1) CNMF::fit_transform [1/100] Loss = nan frobenius norm nan II 0 13:43:09.997 dimension reduction test (EURUSD,H1) CNMF::fit_transform [2/100] Loss = nan frobenius norm nan FG 0 13:43:09.997 dimension reduction test (EURUSD,H1) CNMF::fit_transform [3/100] Loss = nan frobenius norm nan KF 0 13:43:09.997 dimension reduction test (EURUSD,H1) CNMF::fit_transform [4/100] Loss = nan frobenius norm nan PD 0 13:43:09.997 dimension reduction test (EURUSD,H1) CNMF::fit_transform [5/100] Loss = nan frobenius norm nan PR 0 13:43:09.998 dimension reduction test (EURUSD,H1) CNMF::fit_transform [6/100] Loss = nan frobenius norm nan KP 0 13:43:09.998 dimension reduction test (EURUSD,H1) CNMF::fit_transform [7/100] Loss = nan frobenius norm nan NO 0 13:43:09.998 dimension reduction test (EURUSD,H1) CNMF::fit_transform [8/100] Loss = nan frobenius norm nan QM 0 13:43:09.998 dimension reduction test (EURUSD,H1) CNMF::fit_transform [9/100] Loss = nan frobenius norm nan MH 0 13:43:09.998 dimension reduction test (EURUSD,H1) CNMF::fit_transform [10/100] Loss = nan frobenius norm nan .... .... LM 0 13:43:10.006 dimension reduction test (EURUSD,H1) CNMF::fit_transform [97/100] Loss = nan frobenius norm nan OO 0 13:43:10.006 dimension reduction test (EURUSD,H1) CNMF::fit_transform [98/100] Loss = nan frobenius norm nan NI 0 13:43:10.006 dimension reduction test (EURUSD,H1) CNMF::fit_transform [99/100] Loss = nan frobenius norm nan CI 0 13:43:10.006 dimension reduction test (EURUSD,H1) CNMF::fit_transform [100/100] Loss = nan frobenius norm nan MI 0 13:43:10.008 dimension reduction test (EURUSD,H1) NMF Reduced matrix[100x56] FN 0 13:43:10.008 dimension reduction test (EURUSD,H1) [[nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan] EF 0 13:43:10.008 dimension reduction test (EURUSD,H1) [nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan] GK 0 13:43:10.008 dimension reduction test (EURUSD,H1) [nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan] QO 0 13:43:10.008 dimension reduction test (EURUSD,H1) [nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan] CL 0 13:43:10.008 dimension reduction test (EURUSD,H1) ... .... EO 0 13:43:10.008 dimension reduction test (EURUSD,H1) [nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan,nan…] EL 0 13:43:10.010 dimension reduction test (EURUSD,H1) Train acc = nan GJ 0 13:43:10.010 dimension reduction test (EURUSD,H1) Test acc = nan
Versuchen wir, ein lineares Regressionsmodell ohne verkürzte SVD zu erstellen, wenden wir einfach die gesamten Daten darauf an und beobachten wir, wie es abschneidet.
GM 0 13:53:03.686 dimension reduction test (EURUSD,H1) None Reduced matrix[100x56] MG 0 13:53:03.686 dimension reduction test (EURUSD,H1) [[1.099900334222465,28.09636760954466,23.62682944559725,20.05254468697356,24.9034642580335,25.12500390358301,19.04617822178984,1.098553499999958,1.102834674021181,1.094272325978734,1.100734208567449,1.100855469999989,1.098655958571417,1.100133799959087,1.09983,1.097395,1.0950725,1.094895,1.10265,1.100030000000004,1.09944087984,0.03659425270713104,1.100626095746222,1.098825209694279,0.001265714285714323,1.705459946510501e-05,0.0009170545994650059,1655.083284093067,24.54629344924639,0.4388379204892836,0.1040346153847089,0.001226921314023466,0.0012463900886654,100.1775875415509,-1.946877464193406e-05,63.53135141907871,0.1040413928121892,0.1171616554839711,43.66576819407196,56.26437671196908,0.000170982627085528,-39.78494623655773,-2966278.270646845,59.66122501825306,-426422,2459,-0.0002127529411762598,1.096805768175659,1.098423909197834,1.099767192241293,0.00330055882353042,1.797693134862316e+308,1.797693134862316e+308,0.001618141022174502,0,0.03660024400162265] DH 0 13:53:03.687 dimension reduction test (EURUSD,H1) [1.099895090784212,25.44125240854614,20.47658551951762,17.37887206204375,24.10764337690182,24.31185250851098,18.42976333679036,1.098807999999958,1.102730359493936,1.09488564050598,1.100648597660533,1.100904089999989,1.09870448142856,1.100085345856641,1.09983,1.097395,1.0949775,1.09511,1.10237,1.100145000000004,1.09954,0.03659633771631932,1.100539015261062,1.098860393123325,0.001167857142857174,0.000137475370969975,0.0006774753709699599,1151.094538712408,-2.654176423441059,0.4388379204892836,0.1582615384614039,0.001148578761165142,0.001262448000841409,100.0618688017469,-0.0001138692396762668,61.34588689321424,0.1137518684603838,0.1082289779011129,39.39899833055219,47.44710420521373,0.000170240277350424,-32.25806451612595,-2966207.715091289,53.52331983100873,-424517,1905,-0.0003920588235292355,1.097045324469839,1.098718420548105,1.099909753793035,0.003008823529412785,1.797693134862316e+308,1.797693134862316e+308,0.001673096078265379,0,0.0283464566929126] LG 0 13:53:03.687 dimension reduction test (EURUSD,H1) [1.099896454740888,23.0468607955726,17.74637411691527,20.61724467599245,23.13044479515374,23.58127757886977,19.12803587728702,1.099111999999958,1.102374285088665,1.095849714911251,1.100636052620929,1.100962719999989,1.098762994285703,1.100079584777576,1.09983,1.097395,1.0949025,1.09511,1.10224,1.100252000000004,1.10126,0.03659849012444888,1.10032475011848,1.098869304036258,0.001062857142857168,-6.787825345444531e-05,0.0004021217465455251,385.6853260090575,21.57900929644156,0.4735973597359621,0.1358284615387142,0.001095648513071756,0.001261794377734486,100.0745976729165,-0.00016614586466273,63.02688593246703,0.1054308010829696,0.1073759442661703,21.12676056338241,34.73050902933566,0.000167907541851923,-45.79710144927351,-2967636.417218948,63.24364017027852,-427004,2487,-0.0004969529411762387,1.097296453356775,1.098949867979591,1.099885803034428,0.002709058823530563,1.797693134862316e+308,1.797693134862316e+308,0.001653414622816651,1,0.0188982710092469] OH 0 13:53:03.687 dimension reduction test (EURUSD,H1) [1.09988711983821,22.27698129412946,15.38019090132657,21.80270494870316,22.00511532835773,22.64977536234809,19.53807060936342,1.099376999999958,1.101815803805105,1.096938196194811,1.100524122300143,1.101012769999989,1.098812944285703,1.100014455800224,1.099825,1.097395,1.09474,1.09511,1.10151,1.100228000000004,1.1012264,0.03660061924403133,1.100053014395182,1.098898955035223,0.0009950000000000245,-0.0002124670743897106,0.0003975329256102889,-665.9989270069636,-29.795012402167,0.4599358974358811,0.1292584615385153,0.001012177253020718,0.001241318811166551,100.0636954266684,-0.000229141558145832,59.22581938383797,0.05654610290371272,0.09982547246710144,18.13186813187058,26.21920900860187,0.0001634553208976355,-53.91304347826081,-2969847.417218948,53.21227207754287,-429215,2211,-0.000519241176470371,1.097569033867792,1.099141134482142,1.099908642427543,0.002445970588236479,1.797693134862316e+308,1.797693134862316e+308,0.001572100614350314,1,0.02758932609678876] HJ 0 13:53:03.687 dimension reduction test (EURUSD,H1) [1.099803229128606,19.89136498265082,20.62876885414336,18.89567762220941,21.68993269258447,25.44873831711815,17.83416777391867,1.099577499999958,1.101202281523733,1.097952718476183,…] EK 0 13:53:03.689 dimension reduction test (EURUSD,H1) Train acc = -nan MR 0 13:53:03.689 dimension reduction test (EURUSD,H1) Test acc = -nan
Es gibt einige Maßnahmen, die ergriffen werden können, um die Probleme dieser Dimensionsreduktionstechniken anzugehen, wie z.B. die Normalisierung der Eingabedaten, die Behebung numerischer Instabilitäten und vieles mehr, das wir in den nächsten Artikeln besprechen werden. Sie können die Aktualisierungen und zukünftigen Änderungen an diesen Bibliotheken, die in diesem Artikel besprochen werden, immer auf diesem GitHub Repo verfolgen:
Schauen wir uns die Vor- und Nachteile jeder Technik zur Verringerung der Dimensionen an:
Vorteile der verkürzten Singulärwertzerlegung (SVD)
Beibehaltung der Varianz:
SVD zielt darauf ab, so viel Varianz wie möglich in den Originaldaten zu erhalten. Sie bietet eine Möglichkeit, die Daten in einem niedriger-dimensionalen Raum darzustellen, wobei die wichtigsten Informationen erhalten bleiben.
Orthogonalität der Komponenten:
Die durch SVD erhaltenen Komponenten (singuläre Vektoren) sind orthogonal, was bei bestimmten Anwendungen von Vorteil sein kann. Die Orthogonalität vereinfacht die Interpretation der Komponenten.
Numerische Stabilität:
Die SVD ist für ihre numerische Stabilität bekannt. Sie kann mit dünnbesetzten und verrauschten Daten gut umgehen. Die Zerlegung basiert auf der Eigenwertzerlegung der Kovarianzmatrix.
Anwendungen in der Bildkomprimierung und -entrauschung:
SVD wird häufig bei der Bildkomprimierung und -entrauschung eingesetzt. Die Singulärwerte sind ein Maß für die Wichtigkeit, und das Abschneiden dieser Werte ermöglicht eine Komprimierung bei gleichzeitiger Minimierung des Informationsverlustes.
Vorteile der nichtnegativen Matrixzerlegung (NMF)
Teilebasierte Repräsentation:
Die NMF erzwingt Nicht-Negativitätsbeschränkungen sowohl für die Basismatrix als auch für die Koeffizientenmatrix. Dies führt zu einer teilbasierten Darstellung, die in Szenarien von Vorteil sein kann, in denen teilbasierte Merkmale sinnvoll sind (z. B. bei der Themenmodellierung oder der Bildanalyse).
Interpretierbarkeit:
Die Einschränkung der Nicht-Negativität führt häufig zu besser interpretierbaren Faktoren. Bei Themen, die aus Textdaten extrahiert werden, wird beispielsweise jedes Thema als nicht-negative lineare Kombination von Wörtern dargestellt, wodurch die Themen besser interpretierbar werden.
Anwendungen in der Dokumentenanalyse und Bildverarbeitung:
NMF wird häufig in der Dokumentenanalyse (Themenmodellierung) und der Bildverarbeitung eingesetzt. Sie kann zugrundeliegende Muster in Daten erkennen und ist besonders nützlich, wenn die Daten natürlich nicht-negative Komponenten haben.
Dünnbesetzte Repräsentationen:
Die NMF neigt dazu, dünnbesetzte Darstellungen zu erzeugen, bei denen nur eine Teilmenge der Komponenten zur Darstellung jedes Datenpunktes verwendet wird. Dies kann beim Umgang mit hochdimensionalen Daten von Vorteil sein.
Gemeinsame Vorteile
Dimensionsreduktion:
Sowohl SVD als auch NMF bieten wirksame Techniken zur Verringerung der Dimensionalität von Daten, was für den Umgang mit hochdimensionalen Datensätzen und die Extraktion aussagekräftiger Merkmale entscheidend sein kann.
Merkmalsextraktion:
Sie können zur Merkmalsextraktion verwendet werden und ermöglichen die Identifizierung wichtiger Muster oder Merkmale in den Daten.
Rauschunterdrückung:
Beide Techniken können bei der Entrauschung von Daten helfen, indem sie die wesentlichen Informationen erfassen und das Rauschen herausfiltern.
Nachteile der verkürzten Singulärwertzerlegung (SVD)
Empfindlich gegenüber Ausreißern:
Die SVD kann empfindlich auf Ausreißer in den Daten reagieren, da sie versucht, die Summe der quadratischen Fehler zu minimieren. Ausreißer können einen erheblichen Einfluss auf die Zerlegung haben.
Berechnungskomplexität:
Die Berechnung der vollständigen SVD kann rechenintensiv sein, insbesondere bei großen Datensätzen. Die verkürzte SVD bietet eine Annäherung, kann aber bei hochdimensionalen Daten immer noch sehr anspruchsvoll sein.
Begrenzte Anwendbarkeit bei dünnbesetzten Daten:
Die SVD ist bei sehr dünnbesetzten Daten möglicherweise nicht so effektiv, da das Vorhandensein vieler Nullwerte die Genauigkeit der Zerlegung beeinträchtigen kann.
Mangelnde Interpretierbarkeit:
Obwohl die aus der SVD gewonnenen Komponenten orthogonal sind, kann die Interpretierbarkeit dieser Komponenten schwierig sein, insbesondere im Vergleich zu NMF, die eine Nicht-Negativitätsbeschränkungen erzwingt.
Nachteile der nichtnegativen Matrixzerlegung (NMF)
Nicht-Einheitlichkeit der Lösungen:
NMF-Lösungen sind nicht eindeutig, was bedeutet, dass unterschiedliche Initialisierungen zu unterschiedlichen Faktorisierungen führen können. Dieser Mangel an Eindeutigkeit kann es schwierig machen, die Ergebnisse zwischen verschiedenen Läufen zu vergleichen.
Schwierigkeit mit Nulleinträgen:
Die NMF kann bei Nulleinträgen in der Datenmatrix Schwierigkeiten haben. Der Umgang mit fehlenden Daten oder Nullwerten erfordert besondere Überlegungen wie das Entfernen von nan- und Infinity-Werten.
void CDimensionReductionHelpers::ReplaceNaN(matrix &mat) { for (ulong i = 0; i < mat.Rows(); i++) for (ulong j = 0; j < mat.Cols(); j++) if (!MathIsValidNumber(mat[i][j])) mat[i][j] = 0.0; }
Wahl des Ranges (Anzahl der Komponenten):
Die Bestimmung des geeigneten Rangs (Anzahl der Komponenten) für die NMF kann eine Herausforderung sein. Eine ungeeignete Wahl kann zu einer Über- oder Unteranpassung der Daten führen.
Begrenzte Anwendbarkeit auf negative Werte:
Die NMF erzwingt Nicht-Negativität, was für Datensätze, in denen negative Werte von Bedeutung sind, möglicherweise nicht geeignet ist. Diese Einschränkung schränkt die Arten von Daten ein, die effektiv modelliert werden können.
Gemeinsame Überlegungen
Interpretierbarkeit vs. Rekonstruktionsgenauigkeit:
Die NMF kann mehr interpretierbare Komponenten liefern, aber dies geht oft auf Kosten der Rekonstruktionsgenauigkeit im Vergleich zur SVD. Die Wahl zwischen Interpretierbarkeit und Genauigkeit hängt von den spezifischen Zielen der Analyse ab.
Kompromisse bei der Dimensionsreduktion
Bei beiden Techniken besteht ein Kompromiss zwischen der Verringerung der Dimensionen und dem Verlust von Informationen. Die Herausforderung besteht darin, ein optimales Gleichgewicht zu finden, das wesentliche Merkmale bewahrt und gleichzeitig den Informationsverlust minimiert.
Algorithmische Hyperparameter:
Sowohl bei SVD als auch bei NMF kann es erforderlich sein, Hyperparameter wie die Anzahl der Komponenten oder die Stärke der Regularisierung anzupassen, um optimale Ergebnisse zu erzielen. Die Empfindlichkeit gegenüber diesen Hyperparametern sollte berücksichtigt werden.
FAQs zur Dimensionsreduktion
Frage: Wie funktionieren Techniken zur Dimensionsreduktion?
Antwort: Sie wandeln die Daten in einen neuen Satz unkorrelierter variabler Komponenten um, die die maximale Varianz in den ursprünglichen Daten erfassen. Sie ermitteln die Richtungen, in denen die Daten am stärksten variieren.
Frage: Wann sollte ich die Dimensionsreduktion anwenden?
Antwort: Die Dimensionsreduktion ist bei der Arbeit mit hochdimensionalen Daten nützlich, z. B. beim maschinellen Lernen, bei der Bildverarbeitung und in der Bioinformatik. Dies ist von Vorteil, wenn redundante oder irrelevante Merkmale vorhanden sind und die Effizienz der Berechnung, die Interpretierbarkeit oder die Visualisierung im Vordergrund stehen.
Frage: Kann die Dimensionsreduktion auf jede Art von Daten angewendet werden?
Antwort: Die Dimensionsreduktion kann auf verschiedene Datentypen angewendet werden, darunter numerische, kategoriale und Textdaten. Die Wahl der Technik und die Überlegungen können jedoch je nach Art der Daten variieren.
Frage: Gibt es Alternativen zu linearen Dimensionsreduktionsverfahren?
Antwort: Ja, es gibt nichtlineare Techniken wie Kernel-PCA, t-SNE und Autoencoder, die komplexe Beziehungen in den Daten über lineare Transformationen hinaus erfassen.
Frage: Ist die Dimensionsreduktion beim maschinellen Lernen immer von Vorteil?
Antwort: Nicht unbedingt. Die Dimensionsreduktion kann zwar Vorteile in Bezug auf die Recheneffizienz, die Interpretierbarkeit und die Visualisierung bieten, verbessert aber nicht immer die Modellleistung. Sie hängt von den spezifischen Merkmalen des Datensatzes und der Aufgabe des maschinellen Lernens ab.
Frage: Kann die Dimensionsreduktion Informationsverluste verursachen?
Antwort: Ja, die Dimensionsreduktion kann zu Informationsverlusten führen, insbesondere wenn die reduzierte Darstellung relevante Merkmale ausschließt. Ziel ist es, ein Gleichgewicht zwischen der Verringerung der Dimensionalität und der Beibehaltung wesentlicher Informationen zu finden.
Frage: Was sind die Herausforderungen bei Techniken zur Dimensionsreduktion?
Antwort: Zu den Herausforderungen gehören die mögliche Überanpassung, die Empfindlichkeit gegenüber Ausreißern, die Nicht-Eindeutigkeit der Lösungen (insbesondere bei NMF) und die Notwendigkeit einer sorgfältigen Abstimmung der Hyperparameter.
Anhänge:
| Datei | Beschreibung/Verwendung |
|---|---|
| helpers.mqh | Enthält Code zur Unterstützung von Dimensionsreduktionsoperationen, die sowohl in NMF.mqh als auch in TruncatedSVD.mqh stattfinden |
| Linear Regression.mqh | Enthält den Code für das lineare Regressionsmodell |
| matrix_utils.mqh | Zusätzliche Matrixoperationen |
| metrics.mqh | Eine Bibliothek mit Code zur Messung der Leistung von Modellen des maschinellen Lernens |
| NMF | Enthält die Klasse der nichtnegativen Matrixzerlegung |
| plots.mqh | Eine Bibliothek zum Zeichnen von Plots auf dem aktuellen Diagramm |
| preprocessing.mqh | Eine Klasse mit Funktionen zur Vorverarbeitung von Daten, um sie für maschinelles Lernen geeignet zu machen |
| TruncatedSVD.mqh | Enthält die Klasse Truncated SVD |
| dimension reduction test.mq5 | Ein Skript zum Testen des gesamten im Artikel besprochenen Codes |
Peace out.
Übersetzt aus dem Englischen von MetaQuotes Ltd.
Originalartikel: https://www.mql5.com/en/articles/13968
 Algorithmischer Handel mit MetaTrader 5 und R für Einsteiger
Algorithmischer Handel mit MetaTrader 5 und R für Einsteiger
 Anzeige historischer Positionen auf dem Chart als deren Gewinn/Verlust-Diagramm
Anzeige historischer Positionen auf dem Chart als deren Gewinn/Verlust-Diagramm
 Einführung in MQL5 (Teil 2): Navigieren zwischen vordefinierten Variablen, gebräuchlichen Funktionen und Kontrollflussanweisungen
Einführung in MQL5 (Teil 2): Navigieren zwischen vordefinierten Variablen, gebräuchlichen Funktionen und Kontrollflussanweisungen
 Farbpuffer in Multi-Symbol-Multi-Perioden-Indikatoren
Farbpuffer in Multi-Symbol-Multi-Perioden-Indikatoren
- Freie Handelsapplikationen
- Über 8.000 Signale zum Kopieren
- Wirtschaftsnachrichten für die Lage an den Finanzmärkte
Sie stimmen der Website-Richtlinie und den Nutzungsbedingungen zu.